img_cropped = img.crop(box)
img_cropped
¿Qué es una red neuronal tipo MLP?
Las redes neuronales de perceptrones multicapa (MLP, por sus siglas en inglés) son un tipo de modelo de aprendizaje supervisado en Machine Learning. Están compuestas por múltiples capas de nodos (neuronas artificiales) que transforman los datos de entrada mediante funciones de activación no lineales, lo que les permite aprender relaciones complejas entre las variables.
Tipos de modelos MLP
¿Cómo funcionan?
Las redes MLP funcionan ajustando los pesos de las conexiones entre neuronas mediante un proceso de entrenamiento (backpropagation), minimizando el error entre la salida predicha y el valor real. Gracias a sus múltiples capas ocultas, pueden modelar relaciones no lineales complejas.
Ventajas de las Redes Neuronales MLP:
Aplicaciones en Data Analytics Empresarial:
En resumen, las redes MLP ofrecen una alternativa potente y flexible para resolver problemas predictivos complejos en contextos empresariales.
MLPClassifier:
MLPRegressor:
En Machine Learning, las variables predictoras son las entradas del modelo, mientras que la variable objetivo es lo que se desea predecir. Las redes MLP pueden utilizar tanto variables numéricas como categóricas (previa codificación).
Ejemplo de clasificación (MLPClassifier):
Ejemplo de regresión (MLPRegressor):
La predicción del nivel de humedad en granos es fundamental para garantizar la calidad, seguridad y rentabilidad del producto.
Datos:
Tratamiento del problema:
Importancia del problema:
En este contexto, las redes neuronales permiten modelar relaciones complejas entre las características visuales y la variable objetivo, con alta capacidad de generalización para nuevos lotes de grano.
import numpy as np
import matplotlib.pyplot as plt
import seaborn as sns
import pandas as pd
from PIL import Image
import warnings
warnings.filterwarnings("ignore", category=FutureWarning, module="seaborn")
# Descargar imagen
!wget https://raw.githubusercontent.com/marsgr6/ml-online/main/data/H14_093304.jpg
# Nuestra imagen está en escala de grises
img = Image.open('H14_093304.jpg') # cargar imagen
img.size # tamaño de la imagen
--2025-06-20 22:37:20-- https://raw.githubusercontent.com/marsgr6/ml-online/main/data/H14_093304.jpg Resolving raw.githubusercontent.com (raw.githubusercontent.com)... 185.199.108.133, 185.199.109.133, 185.199.110.133, ... Connecting to raw.githubusercontent.com (raw.githubusercontent.com)|185.199.108.133|:443... connected. HTTP request sent, awaiting response... 200 OK Length: 3439002 (3.3M) [image/jpeg] Saving to: ‘H14_093304.jpg’ H14_093304.jpg 100%[===================>] 3.28M --.-KB/s in 0.09s 2025-06-20 22:37:21 (34.8 MB/s) - ‘H14_093304.jpg’ saved [3439002/3439002]
(4128, 3096)
# obtenemos el centro de la imagen
w, h = (np.array(img.size) // 2)
w, h
(np.int64(2064), np.int64(1548))
# Recorte de la imagen, a partir del centro
# nuevas dimensiones (tamaño de recorte)
cw, ch = 660, 660 # nuevo tamaño
# recorte a partir del centro mitad nueveo alto/ancho
box = (w-cw)//2, (h-ch)//2, (w+cw)//2, (h+ch)//2
box # caja de recorte
(np.int64(702), np.int64(444), np.int64(1362), np.int64(1104))
img_cropped = img.crop(box)
img_cropped
El histograma se visualiza como una gráfica de barras, donde el eje $x$ representa los valores de intensidad y el eje Y representa el número de píxeles (frecuencia) para cada valor de intensidad.
El número de bins es un parámetro que se puede elegir, pero un valor común es 256 (panel izquierdo), lo que significa que se crea un bin para cada valor de intensidad posible.
Los valores de intensidad de los píxeles, que normalmente van de 0 a 255 en imágenes de 8 bits, se dividen en un número determinado de intervalos o "bins", en nuestro ejemplo se usan 44 bines (panel izquierdo).
# Transformar array 2D a 1D
pixels = np.array(img_cropped).flatten()
# Construir diagrama de barras con 256 bins
# En una imagen en escala de grises cada pixel contiente un valor entre 0 y 255
plt.figure(figsize=(16,4))
plt.subplot(1,2,1)
plt.bar(*np.unique(pixels, return_counts=True))
# Construir histograma con 44 bins
plt.subplot(1,2,2)
h = plt.hist(pixels, bins=44, density=True)
El modelo MLP utilizará como entrada (X) los histogramas de imágenes en escala de grises obtenidas a partir de fotografías de granos de arroz. Cada histograma se calcula utilizando la altura de los 44 bines, lo que representa la distribución de intensidades de gris en cada imagen. Por lo tanto, la matriz de entrada X tendrá una forma de (n_muestras, 44).
La variable objetivo (y) es el nivel de humedad del grano correspondiente a cada imagen, un valor entero que varía en el rango de 10 a 16. Dependiendo del enfoque, este problema puede ser tratado como:
MLPClassifier, donde cada clase representa un nivel de humedad discreto.MLPRegressor, donde la predicción continua ŷ se redondea al entero más cercano para estimar la clase de humedad.# Las alturas de histograma serán nuestro vector de entrada X
h[0], len(h[0]) # h[0] altura del histograma
(array([5.12741629e-07, 5.12741629e-07, 3.41827753e-07, 1.02548326e-06,
8.54569382e-07, 3.41827753e-07, 1.88005264e-06, 2.73462202e-06,
8.03295220e-06, 1.38440240e-05, 3.07644978e-05, 4.73431438e-05,
1.28869063e-04, 2.84400690e-04, 8.17822899e-04, 1.21143756e-03,
3.46835530e-03, 6.10282179e-03, 1.26272881e-02, 1.23071664e-02,
1.59009725e-02, 1.32940231e-02, 1.51592063e-02, 1.86865269e-02,
1.59177221e-02, 2.41721786e-02, 1.85884223e-02, 1.79866345e-02,
1.22408518e-02, 1.00483686e-02, 4.42991676e-03, 3.49399238e-03,
2.36818267e-03, 2.68915893e-03, 2.03660975e-03, 2.36647353e-03,
1.96192039e-03, 1.90962074e-03, 1.26766822e-03, 1.07641559e-03,
4.38052265e-04, 2.10053154e-04, 4.35830385e-05, 7.34929669e-06]),
44)
data = pd.read_csv('https://raw.githubusercontent.com/marsgr6/r-scripts/master/data/G03_cropG_H_660_660_44_bins.csv')
data.humidity = data.humidity.astype(str)
data.head()
| 0 | 1 | 2 | 3 | 4 | 5 | 6 | 7 | 8 | 9 | ... | 35 | 36 | 37 | 38 | 39 | 40 | 41 | 42 | 43 | humidity | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 0 | 0.0 | 0.0 | 0.0 | 0.000000 | 0.0 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.00000 | ... | 0.012158 | 0.044333 | 0.354619 | 0.098181 | 0.124926 | 0.136753 | 0.008118 | 0.000009 | 0.000000 | 10 |
| 1 | 0.0 | 0.0 | 0.0 | 0.000000 | 0.0 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.00000 | ... | 0.014039 | 0.018889 | 0.141064 | 0.151785 | 0.089501 | 0.119041 | 0.040481 | 0.001417 | 0.000000 | 10 |
| 2 | 0.0 | 0.0 | 0.0 | 0.000000 | 0.0 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.00000 | ... | 0.018064 | 0.023848 | 0.141680 | 0.120306 | 0.108169 | 0.121783 | 0.027558 | 0.000676 | 0.000000 | 10 |
| 3 | 0.0 | 0.0 | 0.0 | 0.000000 | 0.0 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.00000 | ... | 0.029847 | 0.022650 | 0.035885 | 0.074686 | 0.087595 | 0.107312 | 0.082734 | 0.014666 | 0.000054 | 10 |
| 4 | 0.0 | 0.0 | 0.0 | 0.000009 | 0.0 | 0.000009 | 0.000027 | 0.000018 | 0.000045 | 0.00009 | ... | 0.015860 | 0.043084 | 0.339896 | 0.143472 | 0.115284 | 0.128973 | 0.035604 | 0.001162 | 0.000000 | 10 |
5 rows × 45 columns
data.iloc[:,:-1].describe()
| 0 | 1 | 2 | 3 | 4 | 5 | 6 | 7 | 8 | 9 | ... | 34 | 35 | 36 | 37 | 38 | 39 | 40 | 41 | 42 | 43 | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| count | 218.000000 | 218.000000 | 218.000000 | 218.000000 | 218.000000 | 218.000000 | 218.000000 | 218.000000 | 218.000000 | 218.000000 | ... | 218.000000 | 218.000000 | 218.000000 | 218.000000 | 218.000000 | 218.000000 | 218.000000 | 218.000000 | 218.000000 | 218.000000 |
| mean | 0.000014 | 0.000028 | 0.000065 | 0.000128 | 0.000214 | 0.000966 | 0.005213 | 0.001067 | 0.000116 | 0.000171 | ... | 0.027661 | 0.031278 | 0.087876 | 0.190515 | 0.112837 | 0.103457 | 0.116627 | 0.032822 | 0.001430 | 0.000002 |
| std | 0.000114 | 0.000201 | 0.000394 | 0.000689 | 0.001124 | 0.007024 | 0.035924 | 0.006590 | 0.000315 | 0.000339 | ... | 0.023420 | 0.031301 | 0.091787 | 0.095035 | 0.032029 | 0.020023 | 0.048207 | 0.023983 | 0.002411 | 0.000012 |
| min | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | ... | 0.007444 | 0.007756 | 0.011540 | 0.028937 | 0.037259 | 0.043105 | 0.007829 | 0.000086 | 0.000000 | 0.000000 |
| 25% | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | ... | 0.012980 | 0.014053 | 0.027827 | 0.125638 | 0.089162 | 0.090107 | 0.082844 | 0.010775 | 0.000047 | 0.000000 |
| 50% | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000015 | ... | 0.020033 | 0.019908 | 0.046835 | 0.171026 | 0.108850 | 0.102421 | 0.123879 | 0.030658 | 0.000638 | 0.000000 |
| 75% | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000000 | 0.000033 | 0.000081 | 0.000188 | ... | 0.028884 | 0.037133 | 0.108597 | 0.247400 | 0.133112 | 0.114255 | 0.151436 | 0.049145 | 0.001721 | 0.000000 |
| max | 0.001474 | 0.002317 | 0.003440 | 0.004835 | 0.009255 | 0.090649 | 0.377729 | 0.075797 | 0.002356 | 0.001916 | ... | 0.141751 | 0.253941 | 0.415862 | 0.537803 | 0.236872 | 0.181483 | 0.234865 | 0.116686 | 0.018232 | 0.000134 |
8 rows × 44 columns
data.iloc[:,:-1].shape
(218, 44)
Este heatmap visualiza el dataset completo de histogramas de imágenes en escala de grises, usado como entrada para el modelo MLP.
H=10 a H=16).H=10 a H=16), marcados por líneas verticales color cian.H=10 a H=16).H=13 o H=14) presentan patrones más definidos en la distribución del histograma.Este heatmap es útil para visualizar cómo varían las distribuciones de intensidad de gris según la humedad del grano. La información relevante para el modelo MLP se encuentra principalmente en los bins 12 a 42, mientras que las colas (bins bajos y altos) podrían ser candidatas a ser descartadas o recibir menor ponderación en modelos más complejos.
plt.figure(figsize=(12,6))
sns.heatmap(data.iloc[:,:-1].T)
t = list(data.humidity.unique())
x = list(data.humidity.value_counts().cumsum())
c = list(data.humidity.value_counts())
plt.vlines(x,
data.humidity.nunique()*[0],
data.shape[0]*data.humidity.nunique(), colors="cyan")
plt.hlines([12.5, 42.5], [0, 0], [218, 218], colors="yellow")
[plt.text(v[0]-v[2]//2-6, 2, 'H='+v[1], c='white', fontweight="bold") for v in zip(x, t, c)];
plt.text(5, 12, 'Bin 12', c='white', fontweight="bold");
plt.text(5, 42, 'Bin 42', c='white', fontweight="bold");
plt.show()
Un problema de clasificación multi-clase balanceado se refiere a una tarea de aprendizaje automático donde se busca clasificar datos en diferentes categorías, teniendo en cuenta que cada categoría tiene un número similar de ejemplos.
En este tipo de problemas, la distribución de las clases es uniforme o casi uniforme, a diferencia de los problemas desbalanceados donde una o pocas clases son dominantes.
Características:
En un problema de clasificación multi-clase desbalanceado, un modelo sin técnicas de balanceo puede:
Técnicas de Balanceo:
Para abordar un problema de clasificación multi-clase balanceado, se pueden aplicar diferentes técnicas, como:
ax = sns.countplot(x='humidity', data=data)
ax.bar_label(ax.containers[0]);
plt.figure(figsize=(10,4))
plt.subplot(1,2,1)
sns.boxenplot(data=data, x='humidity', y='20', hue='humidity')
plt.subplot(1,2,2)
sns.boxenplot(data=data, x='humidity', y='22', hue='humidity')
<Axes: xlabel='humidity', ylabel='22'>
plt.figure(figsize=(10,4))
plt.subplot(1,2,1)
sns.kdeplot(data=data, hue='humidity', x='23')
plt.subplot(1,2,2)
sns.kdeplot(data=data, hue='humidity', x='22')
<Axes: xlabel='22', ylabel='Density'>
plt.figure(figsize=(6,4))
sns.scatterplot(data=data, x='22', y='23', hue='humidity')
<Axes: xlabel='22', ylabel='23'>
Vea: https://nbviewer.org/github/marsgr6/EN-online/blob/main/dimensionality_reduction.ipynb
Un proyecto de ML exitoso no se limita a entrenar un modelo con una red neuronal. Requiere una planificación y ejecución cuidadosa en cada etapa para garantizar resultados confiables y adaptables a la realidad del negocio.
1. Definición del objetivo:
2. Recopilación y preparación de datos:
3. Elección del modelo:
4. Entrenamiento del modelo:
5. Evaluación del modelo:
6. Implementación y monitoreo:
7. Documentación y comunicación:
Cada proyecto de ML es único y puede requerir adaptaciones a estos pasos generales. Es importante ser flexible y adaptable a medida que se avanza en el proyecto, y siempre tener en cuenta el objetivo final de resolver un problema real del negocio.
Redes Neuronales MLP (Multilayer Perceptron):
Una red neuronal MLP es un modelo de aprendizaje automático supervisado capaz de realizar tanto tareas de clasificación como de regresión. Está compuesta por múltiples capas de neuronas artificiales conectadas entre sí, donde cada capa transforma los datos de entrada mediante funciones de activación no lineales.
Funcionamiento:
Ventajas:
Desventajas:
En resumen:
1. Definición del objetivo:
2. Recopilación y preparación de datos:
Detalles:
3. Elección del modelo:
Desarrollar dos variantes de MLP:
Para el modelo de regresión:
4. Entrenamiento y 5. Evaluación del modelo:
Ajuste de hiperparámetros:
Métricas:
Visualizaciones:
Referencias:
Determination of Moisture in Rice Grains Based on Visible Spectrum Analysis:
# Seleccionar entrada X y las etiquetas de salida y
X = data.iloc[:,:-1] # todas las columnas menos la etiquieta y
y = data['humidity'] # etiqueta y: humedad
Entrenamos y evaluamos con todos los datos (solo a modo exploratorio):
Los pasos generales a seguir en sklearn para construir un modelo MLPClassifier son:
from sklearn.neural_network import MLPClassifier
clf = MLPClassifier(hidden_layer_sizes=(100,), max_iter=1000, random_state=42)
clf.fit(X, y)
y_pred = clf.predict(X)
from sklearn.metrics import classification_report, confusion_matrix
print(classification_report(y, y_pred))
print(confusion_matrix(y, y_pred))
import numpy as np
import pandas as pd
from sklearn.neural_network import MLPClassifier
from sklearn.metrics import classification_report, confusion_matrix, ConfusionMatrixDisplay
from sklearn.preprocessing import StandardScaler
import matplotlib.pyplot as plt
import seaborn as sns
# --- Cargar datos (X: histogramas, y: humedad entre 10 y 16) ---
# Escalado
scaler = StandardScaler()
X_scaled = scaler.fit_transform(X)
# Definir y entrenar el modelo
clf = MLPClassifier(hidden_layer_sizes=(100,), max_iter=1000, random_state=42)
clf.fit(X_scaled, y)
# Predicción
y_pred = clf.predict(X_scaled)
# Evaluación textual
print("Classification Report:")
print(classification_report(y, y_pred))
# Matriz de confusión
cm = confusion_matrix(y, y_pred, labels=sorted(np.unique(y)))
disp = ConfusionMatrixDisplay(confusion_matrix=cm, display_labels=sorted(np.unique(y)))
# Visualización
fig, ax = plt.subplots(figsize=(8, 6))
disp.plot(ax=ax, cmap='Blues', colorbar=False)
plt.title("Matriz de Confusión - MLPClassifier")
Classification Report:
precision recall f1-score support
10 1.00 1.00 1.00 29
11 1.00 1.00 1.00 31
12 1.00 1.00 1.00 32
13 1.00 1.00 1.00 35
14 1.00 1.00 1.00 31
15 1.00 1.00 1.00 31
16 1.00 1.00 1.00 29
accuracy 1.00 218
macro avg 1.00 1.00 1.00 218
weighted avg 1.00 1.00 1.00 218
Text(0.5, 1.0, 'Matriz de Confusión - MLPClassifier')
Una matriz de confusión es una herramienta fundamental en el aprendizaje automático para evaluar el rendimiento de un modelo de clasificación. Esta matriz resume las predicciones del modelo en comparación con las etiquetas reales de los datos, permitiendo visualizar y comprender los errores del modelo de forma clara y concisa.
Estructura de la matriz:
Cada celda de la matriz contiene el número de instancias que fueron clasificadas en una clase específica por el modelo, en comparación con su clase real.
Ejemplo:
Supongamos que tenemos un problema de clasificación binaria con dos clases: Perro y Gato. La matriz de confusión para un modelo con 100 instancias podría verse así:
| Perro (Predicho) | Gato (Predicho) | Total | |
|---|---|---|---|
| Perro (Real) | 80 | 20 | 100 |
| Gato (Real) | 10 | 90 | 100 |
| Total | 90 | 110 | 200 |
Interpretación de la matriz:
Beneficios de la matriz de confusión:
La evaluación del rendimiento de un modelo de clasificación es crucial para entender su eficacia y limitaciones. Existen diversas métricas utilizadas para este fin, entre las que destacan:
1. Precisión (Precision):
2. Recall (Sensibilidad):
3. F1-Score:
Resumen:
La elección de la métrica más adecuada depende del contexto específico del problema. En general, si las clases están relativamente equilibradas y ambos tipos de error (clasificar mal los positivos y clasificar mal los negativos) son igualmente costosos, entonces la F1-Score puede ser una buena opción. Si un tipo de error tiene un costo mayor que el otro, entonces podría ser más relevante utilizar la precisión o el recall dependiendo del tipo de error que se quiera minimizar.
Calculamos la precisión, recall y F1:
| Perro (Predicho) | Gato (Predicho) | Total | |
|---|---|---|---|
| Perro (Real) | 80 | 20 | 100 |
| Gato (Real) | 10 | 90 | 100 |
| Total | 90 | 110 | 200 |
Precisión:
Recall:
F1:
Interpretación de los resultados:
En nuestro ejemplo un F1-Score de 1 significa que el modelo clasifica perfectamente todas las instancias, sin cometer ningún error.
Esto implica que:
La precisión del modelo es del 100%, lo que significa que todas las instancias predichas como positivas realmente lo son. El recall del modelo también es del 100%, lo que significa que todas las instancias positivas reales fueron correctamente clasificadas.
¿Se ha generalizado bien?
Un F1-Score perfecto en el conjunto de entrenamiento no garantiza que el modelo se generalice bien a nuevos datos que no ha visto antes. Es crucial evaluar el modelo en un conjunto de test independiente para asegurar su rendimiento en situaciones reales.
Un train test split es una técnica fundamental en el aprendizaje automático para dividir un conjunto de datos en dos subconjuntos:
La división del conjunto de datos en dos partes permite:
Existen diferentes técnicas para realizar un train test split:
Validación cruzada: Es una técnica más avanzada que divide los datos en múltiples conjuntos y entrena y evalúa el modelo en cada uno de ellos.
La línea de código:
X_train, X_test, y_train, y_test = train_test_split(X, y, stratify=y)
divide un conjunto de datos en dos conjuntos, un conjunto de entrenamiento y un conjunto de prueba, de forma estratificada. Esto significa que se asegura que la distribución de clases en ambos conjuntos de prueba y entrenamiento sea similar a la distribución de clases en el conjunto de datos original.
stratify=y: Este es el argumento clave que habilita la estratificación. Indica que la división del conjunto de datos debe mantener la misma distribución de clases que el conjunto de datos original. Esto es particularmente importante cuando se trabaja con conjuntos de datos desbalanceados, donde hay una clase dominante y varias clases minoritarias.
El argumento stratify solo funciona con variables objetivo categóricas (clases).
import numpy as np
import pandas as pd
import matplotlib.pyplot as plt
from sklearn.neural_network import MLPClassifier
from sklearn.model_selection import train_test_split
from sklearn.metrics import classification_report, confusion_matrix, ConfusionMatrixDisplay
from sklearn.preprocessing import StandardScaler
# División de los datos en entrenamiento y prueba (estratificado)
X_train, X_test, y_train, y_test = train_test_split(X, y, test_size=0.25, stratify=y, random_state=42)
# Escalado de los datos (muy importante para MLP)
scaler = StandardScaler()
X_train_scaled = scaler.fit_transform(X_train)
X_test_scaled = scaler.transform(X_test)
# Definición y entrenamiento del modelo
clf = MLPClassifier(hidden_layer_sizes=(100,), max_iter=1000, random_state=42)
clf.fit(X_train_scaled, y_train)
# Predicción sobre el conjunto de prueba
y_pred = clf.predict(X_test_scaled)
# Reporte de clasificación
print(classification_report(y_test, y_pred))
# Matriz de confusión
cm = confusion_matrix(y_test, y_pred, labels=sorted(np.unique(y)))
disp = ConfusionMatrixDisplay(confusion_matrix=cm, display_labels=sorted(np.unique(y)))
# Visualización
fig, ax = plt.subplots(figsize=(8, 6))
disp.plot(ax=ax, cmap='Blues', colorbar=False)
plt.title("Matriz de Confusión - MLPClassifier")
precision recall f1-score support
10 1.00 0.57 0.73 7
11 0.73 1.00 0.84 8
12 1.00 1.00 1.00 8
13 1.00 1.00 1.00 9
14 0.89 1.00 0.94 8
15 0.88 0.88 0.88 8
16 1.00 0.86 0.92 7
accuracy 0.91 55
macro avg 0.93 0.90 0.90 55
weighted avg 0.93 0.91 0.91 55
Text(0.5, 1.0, 'Matriz de Confusión - MLPClassifier')
Discuta la matriz de confusión y las métricas de evaluación del modelo.
La clasificación no es perfecta en este caso para nuestro conjunto de prueba. Este es un resultado más realista de lo que observaremos en la implementación del modelo.
Vamos a realizar un ejercicio de validación cruzada en conjunto con la optimización de hiper-parámetros del modelo RF.
La validación cruzada con ajuste de hiperparámetros es una técnica avanzada en el aprendizaje automático que combina dos estrategias para optimizar el rendimiento de un modelo:
1. Validación cruzada (CV):
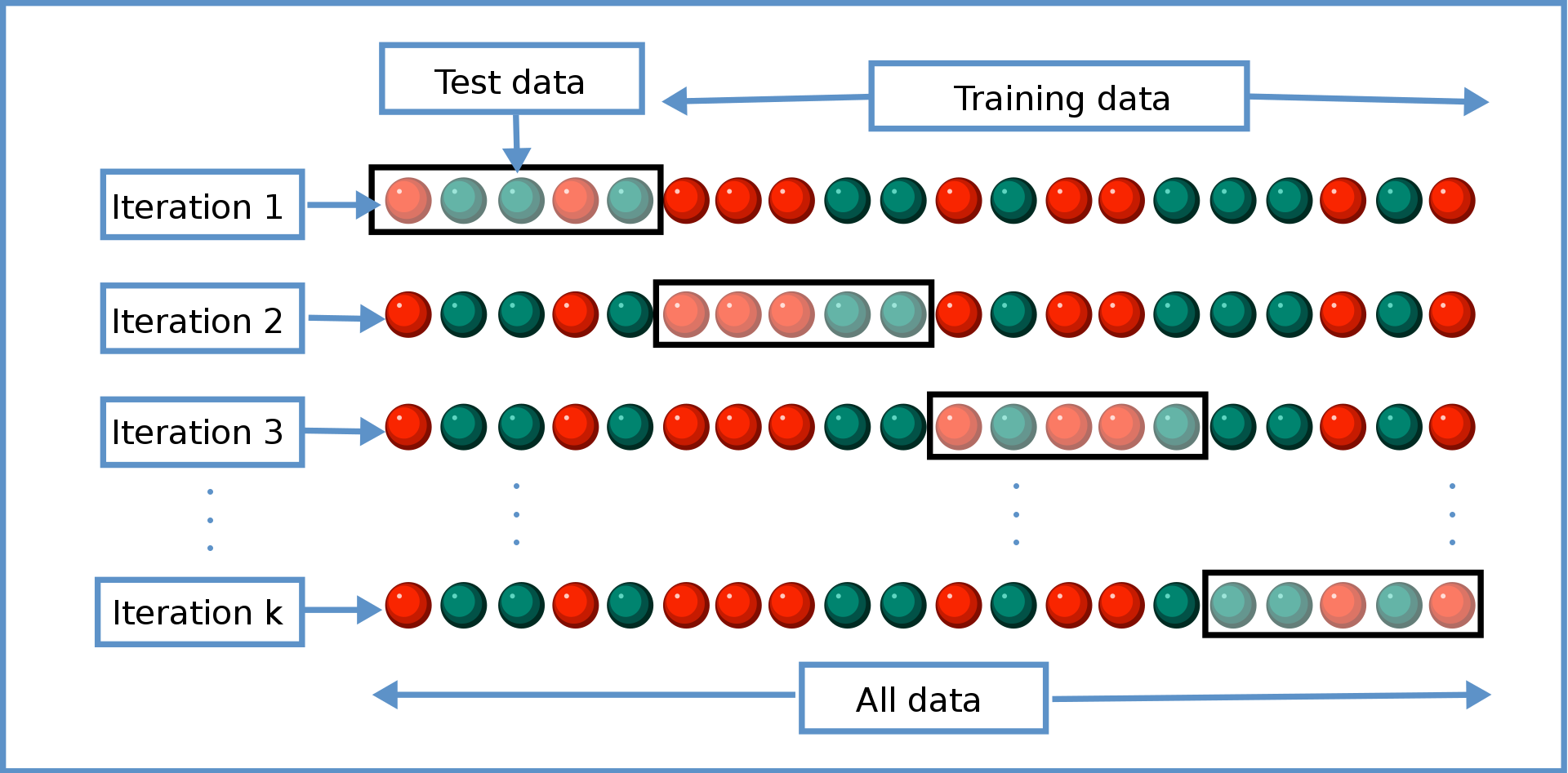
La validación cruzada divide el conjunto de datos en múltiples subconjuntos (folds) y entrena y evalúa el modelo en cada uno de ellos. Esto permite obtener una estimación más precisa del rendimiento del modelo en comparación con la evaluación en un solo conjunto de prueba.
2. Ajuste de hiperparámetros (HPO):
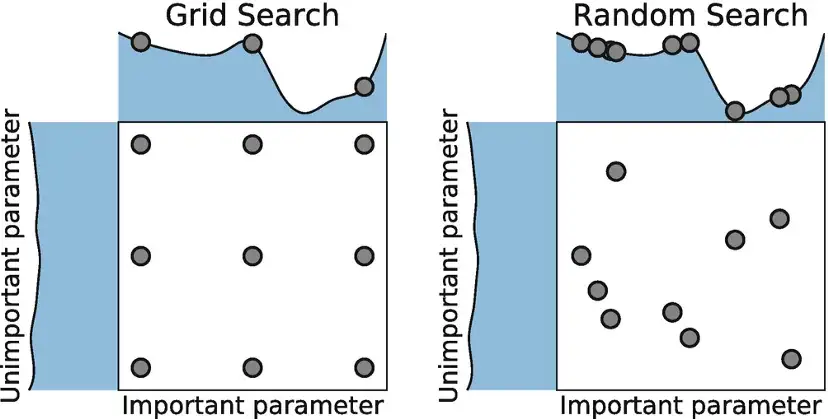
Los hiperparámetros son los parámetros que controlan el proceso de entrenamiento del modelo, como la tasa de aprendizaje o el número de iteraciones. El ajuste de hiperparámetros busca encontrar la mejor configuración de estos parámetros para optimizar el rendimiento del modelo.
Búsqueda aleatoria:
Búsqueda en cuadrícula:
Resumen:
Consideraciones adicionales:
Recomendación:
Se recomienda probar ambas técnicas y comparar sus resultados para elegir la mejor opción para cada caso particular.
Combinación de ambas técnicas (CV y HPO):
La validación cruzada con ajuste de hiperparámetros combina ambas estrategias para encontrar la mejor configuración de hiperparámetros para un modelo. El proceso se realiza de la siguiente manera:
Ventajas de la validación cruzada con ajuste de hiperparámetros:
El número de folds a usar en la validación cruzada (cross validation) depende de varios factores, incluyendo:
1. Tamaño del conjunto de datos:
2. Varianza del modelo:
3. Tiempo de computación:
En general, se recomienda usar un número de folds entre 5 y 30.
Algunos valores comunes son:
Es importante tener en cuenta que no existe un número "óptimo" de folds que funcione para todos los casos.
La mejor manera de determinar el número de folds a usar es experimentar con diferentes valores y observar cómo afecta el rendimiento del modelo.
Algunos consejos adicionales para elegir el número de folds:
Recursos adicionales:
En un modelo de red neuronal MLP, los hiperparámetros que se pueden optimizar incluyen:
1. Tamaño y estructura de la red (hidden_layer_sizes): Define el número de capas ocultas y el número de neuronas en cada capa. Por ejemplo, (100,) indica una sola capa con 100 neuronas, y (100, 50) dos capas con 100 y 50 neuronas respectivamente. Redes más grandes pueden capturar patrones complejos pero también pueden sobreajustar.
2. Función de activación (activation): Controla la no linealidad entre capas. Las opciones comunes son 'relu', 'tanh' y 'logistic'. 'relu' suele ser la más eficiente en la mayoría de los casos.
3. Algoritmo de optimización (solver): Determina el método para actualizar los pesos. Opciones comunes: 'adam', 'lbfgs', 'sgd'. 'adam' es el más utilizado por su buen rendimiento general.
4. Tasa de aprendizaje inicial (learning_rate_init): Controla cuán rápido se actualizan los pesos. Valores muy grandes pueden hacer que la red no converja; valores muy pequeños pueden hacer que el entrenamiento sea lento.
5. Regularización L2 (alpha): Ayuda a prevenir el sobreajuste penalizando pesos grandes. Valores más altos aumentan la regularización.
6. Máximo número de iteraciones (max_iter): Límite de épocas para el entrenamiento. Si el modelo no converge dentro de este límite, se detiene.
7. Estrategia de aprendizaje (learning_rate): Define cómo cambia la tasa de aprendizaje durante el entrenamiento. Por ejemplo: 'constant', 'invscaling' o 'adaptive' (solo con 'sgd').
8. Tamaño del batch (batch_size): Número de ejemplos usados en cada actualización de pesos. Solo se aplica cuando el solver='sgd' o 'adam'.
9. Parámetros de parada temprana (early_stopping, tol, n_iter_no_change): Se usan para detener el entrenamiento si no hay mejora significativa durante varias iteraciones consecutivas.
10. Peso de clases (class_weight): Solo aplica en clasificación. Puede ser 'balanced' para manejar desbalance de clases.
En general, no existe una configuración única de hiperparámetros que funcione mejor para todos los conjuntos de datos. Es importante realizar una búsqueda sistemática (como GridSearchCV o RandomSearchCV) para encontrar la combinación que mejor se adapte a su problema específico.
from sklearn.neural_network import MLPClassifier
from sklearn.model_selection import GridSearchCV
from sklearn.preprocessing import StandardScaler
from sklearn.pipeline import make_pipeline
import pandas as pd
import warnings
warnings.filterwarnings("ignore")
data = pd.read_csv('https://raw.githubusercontent.com/marsgr6/r-scripts/master/data/G03_cropG_H_660_660_44_bins.csv')
data.humidity = data.humidity.astype(str)
# Seleccionar entrada X y las etiquetas de salida y
X = data.iloc[:,:-1] # todas las columnas menos la etiquieta y
y = data['humidity'] # etiqueta y: humedad
# Espacio de búsqueda de hiperparámetros para MLPClassifier dentro de un pipeline
params_MLP = {
'mlpclassifier__hidden_layer_sizes': [(50), (100,), (200,), (500,)],
'mlpclassifier__activation': ['tanh', 'relu'],
'mlpclassifier__learning_rate_init': [0.0001, 0.001, 0.01],
'mlpclassifier__alpha': [0.0001, 0.001, 0.01],
'mlpclassifier__max_iter': [1000]
}
# Pipeline con escalado + MLPClassifier
pipeline = make_pipeline(
StandardScaler(),
MLPClassifier(random_state=42)
)
# GridSearch con validación cruzada
grid_search = GridSearchCV(
estimator=pipeline,
param_grid=params_MLP,
scoring='accuracy', # Métrica: accuracy (clasificación)
cv=5,
verbose=2,
n_jobs=-1
)
# Entrenamiento con todos los datos
grid_search.fit(X, y)
# Mejores hiperparámetros encontrados
print("Mejores hiperparámetros encontrados:")
print(grid_search.best_params_)
# Mejor precisión promedio en validación cruzada
print("\nAccuracy promedio (CV) del mejor modelo:")
print(grid_search.best_score_)
Fitting 5 folds for each of 72 candidates, totalling 360 fits
Mejores hiperparámetros encontrados:
{'mlpclassifier__activation': 'relu', 'mlpclassifier__alpha': 0.0001, 'mlpclassifier__hidden_layer_sizes': (100,), 'mlpclassifier__learning_rate_init': 0.001, 'mlpclassifier__max_iter': 1000}
Accuracy promedio (CV) del mejor modelo:
0.9215644820295983
import pandas as pd
import seaborn as sns
import matplotlib.pyplot as plt
# Convert GridSearchCV results to DataFrame
results_df = pd.DataFrame(grid_search.cv_results_)
# Extract relevant hyperparameters and accuracy
results_df['hidden_layer_sizes'] = results_df['param_mlpclassifier__hidden_layer_sizes'].astype(str)
results_df['activation'] = results_df['param_mlpclassifier__activation'].astype(str)
results_df['alpha'] = results_df['param_mlpclassifier__alpha']
results_df['learning_rate_init'] = results_df['param_mlpclassifier__learning_rate_init']
results_df['mean_test_score'] = results_df['mean_test_score'] # accuracy
# Optional: sort for smoother plots
results_df.sort_values(by=['learning_rate_init', 'alpha'], inplace=True)
# Show first few rows (optional)
results_df[['hidden_layer_sizes', 'activation', 'alpha', 'learning_rate_init', 'mean_test_score']].head()
| hidden_layer_sizes | activation | alpha | learning_rate_init | mean_test_score | |
|---|---|---|---|---|---|
| 0 | 50 | tanh | 0.0001 | 0.0001 | 0.857294 |
| 3 | (100,) | tanh | 0.0001 | 0.0001 | 0.893975 |
| 6 | (200,) | tanh | 0.0001 | 0.0001 | 0.903171 |
| 9 | (500,) | tanh | 0.0001 | 0.0001 | 0.903277 |
| 36 | 50 | relu | 0.0001 | 0.0001 | 0.871036 |
# Graficar usando seaborn.relplot con columnas por tipo de activación
sns.set(style="whitegrid")
g = sns.relplot(
data=results_df,
x="hidden_layer_sizes", y="mean_test_score",
hue="learning_rate_init", style="activation", col="alpha",
kind="line", palette="tab10",
height=5, aspect=0.75
)
plt.tight_layout()
grid_search.best_params_
{'mlpclassifier__activation': 'relu',
'mlpclassifier__alpha': 0.0001,
'mlpclassifier__hidden_layer_sizes': (100,),
'mlpclassifier__learning_rate_init': 0.001,
'mlpclassifier__max_iter': 1000}
mean_test_score.from sklearn.model_selection import cross_val_score
import seaborn as sns
import matplotlib.pyplot as plt
# Supone que ya ejecutaste GridSearchCV y tienes gs_MLP listo
best_MLP = grid_search.best_estimator_
# Define tu método de validación cruzada, por ejemplo con 5 folds estratificados
from sklearn.model_selection import StratifiedKFold
cv_method = StratifiedKFold(n_splits=5, shuffle=True, random_state=42)
# Evaluar el desempeño del mejor modelo con validación cruzada
scores_class = cross_val_score(best_MLP, X, y, cv=cv_method, scoring='accuracy')
# Mostrar resultados
print("Scores (Accuracy por fold):", scores_class)
print("Accuracy promedio:", scores_class.mean())
# Visualización
sns.boxplot(y=scores_class)
plt.title("Distribución de precisión del mejor MLP")
plt.ylabel("Accuracy")
# Mostrar el modelo entrenado final
best_MLP
Scores (Accuracy por fold): [0.93181818 0.95454545 0.97727273 0.88372093 0.90697674] Accuracy promedio: 0.9308668076109935
Pipeline(steps=[('standardscaler', StandardScaler()),
('mlpclassifier',
MLPClassifier(max_iter=1000, random_state=42))])In a Jupyter environment, please rerun this cell to show the HTML representation or trust the notebook. Pipeline(steps=[('standardscaler', StandardScaler()),
('mlpclassifier',
MLPClassifier(max_iter=1000, random_state=42))])StandardScaler()
MLPClassifier(max_iter=1000, random_state=42)
A diferencia de modelos como Random Forest, un MLP (Multilayer Perceptron) no ofrece directamente una métrica de "feature importance" basada en reducción de impureza. Sin embargo, es posible analizar la importancia relativa de las características mediante enfoques como:
Es importante destacar que, en MLP, la interpretación de importancia de características es menos directa e intuitiva que en árboles de decisión, debido a la naturaleza distribuida y no lineal de las representaciones aprendidas.
En nuestro caso, el análisis posterior del modelo entrenado sugiere que ciertos bines del histograma específicamente los bins centrales como 25, 26 y 40 muestran mayor separabilidad entre las clases de humedad. Estos bines, por tanto, podrían tener una mayor influencia en la predicción del modelo y deberían considerarse prioritarios en análisis futuros o en procesos de selección de variables.
# Importación de librerías necesarias
import pandas as pd
import numpy as np
import seaborn as sns
import matplotlib.pyplot as plt
from sklearn.pipeline import make_pipeline
from sklearn.preprocessing import StandardScaler
from sklearn.neural_network import MLPClassifier
from sklearn.model_selection import cross_val_score
from sklearn.inspection import permutation_importance
from sklearn.model_selection import StratifiedKFold
# Cargar el conjunto de datos desde una URL
data = pd.read_csv('https://raw.githubusercontent.com/marsgr6/r-scripts/master/data/G03_cropG_H_660_660_44_bins.csv')
# Convertir la columna 'humidity' en string para clasificación multiclase
data['humidity'] = data['humidity'].astype(str)
# Separar variables predictoras (X) y variable objetivo (y)
X = data.iloc[:, :-1] # Todas las columnas excepto la última
y = data['humidity'] # Columna objetivo: humedad en niveles discretos
# Construir un pipeline con los mejores hiperparámetros encontrados en GridSearchCV
best_mlp = make_pipeline(
StandardScaler(), # Escalado estándar para que las variables tengan media 0 y varianza 1
MLPClassifier( # Clasificador MLP (red neuronal multicapa)
activation='relu', # Función de activación ReLU
alpha=0.0001, # Regularización L2
hidden_layer_sizes=(100,), # Una capa oculta con 100 neuronas
learning_rate_init=0.001, # Tasa de aprendizaje inicial
max_iter=1000, # Número máximo de iteraciones (épocas)
random_state=42 # Semilla para reproducibilidad
)
)
# Entrenar el modelo con todos los datos disponibles
best_mlp.fit(X, y)
# Calcular la importancia de características mediante permutación
perm = permutation_importance(
estimator=best_mlp, # Modelo entrenado
X=X, y=y, # Conjunto de datos completo
n_repeats=30, # Número de repeticiones para estimar la variabilidad
random_state=42, # Semilla aleatoria para reproducibilidad
n_jobs=-1 # Usar todos los núcleos disponibles para acelerar el cálculo
)
# Organizar los resultados en un DataFrame para facilitar su análisis
perm_df = pd.DataFrame({
'Feature': X.columns,
'Importance Mean': perm.importances_mean, # Disminución promedio en la precisión
'Importance Std': perm.importances_std # Desviación estándar de esa disminución
}).sort_values(by="Importance Mean", ascending=False) # Ordenar de mayor a menor importancia
# Visualizar las 15 características más importantes con barras de error
plt.figure(figsize=(10, 6))
data=perm_df.head(15)
plt.errorbar(data['Feature'], data['Importance Mean'], yerr=data['Importance Std'], fmt='-o', capsize=5, color='tab:blue')
plt.title("Top 15 Feature Importances (Permutation)")
plt.ylabel("Mean Decrease in Accuracy")
plt.xlabel(r"Bin (variable $X_i$)")
plt.tight_layout()
Este gráfico representa la importancia de las características del modelo MLP, calculada mediante permutación. La idea es observar cuánto disminuye la precisión del modelo cuando se desordena (permuta) cada característica, una por una.
Esto sugiere que el modelo MLP depende más de esos bines para predecir correctamente el nivel de humedad.
Este análisis puede ayudarte a:
from sklearn.neural_network import MLPClassifier
from sklearn.model_selection import RandomizedSearchCV
from sklearn.preprocessing import StandardScaler
from sklearn.pipeline import make_pipeline
import pandas as pd
import numpy as np
import warnings
warnings.filterwarnings("ignore")
# Cargar datos
data = pd.read_csv('https://raw.githubusercontent.com/marsgr6/r-scripts/master/data/G03_cropG_H_660_660_44_bins.csv')
data.humidity = data.humidity.astype(str)
# Separar variables independientes (X) y variable dependiente (y)
X = data.iloc[:, :-1]
y = data['humidity']
# Espacio de búsqueda para RandomizedSearchCV
params_MLP = {
'mlpclassifier__hidden_layer_sizes': [(50,), (100,), (200,), (300,), (100, 50)],
'mlpclassifier__activation': ['identity', 'logistic', 'tanh', 'relu'],
'mlpclassifier__solver': ['adam', 'sgd'],
'mlpclassifier__alpha': [1e-5, 1e-4, 1e-3, 1e-2],
'mlpclassifier__learning_rate_init': [0.0001, 0.001, 0.01, 0.1],
'mlpclassifier__max_iter': [1000],
'mlpclassifier__learning_rate': ['constant', 'invscaling', 'adaptive']
}
# Pipeline de escalado + MLPClassifier
pipeline = make_pipeline(
StandardScaler(),
MLPClassifier(random_state=42)
)
# RandomizedSearchCV con validación cruzada
random_search = RandomizedSearchCV(
estimator=pipeline,
param_distributions=params_MLP,
n_iter=40, # Número de combinaciones aleatorias a probar
scoring='accuracy',
cv=5,
verbose=2,
random_state=42,
n_jobs=-1
)
# Entrenar
random_search.fit(X, y)
# Resultados
print("🎯 Mejores hiperparámetros encontrados:")
print(random_search.best_params_)
print("\n✅ Mejor precisión promedio en validación cruzada:")
print(random_search.best_score_)
# Convert results to DataFrame
results_df = pd.DataFrame(random_search.cv_results_)
# Sort by mean test score
results_df = results_df.sort_values(by="mean_test_score", ascending=False)
results_df.head()
Fitting 5 folds for each of 40 candidates, totalling 200 fits
🎯 Mejores hiperparámetros encontrados:
{'mlpclassifier__solver': 'adam', 'mlpclassifier__max_iter': 1000, 'mlpclassifier__learning_rate_init': 0.001, 'mlpclassifier__learning_rate': 'constant', 'mlpclassifier__hidden_layer_sizes': (50,), 'mlpclassifier__alpha': 1e-05, 'mlpclassifier__activation': 'logistic'}
✅ Mejor precisión promedio en validación cruzada:
0.9169133192389006
| mean_fit_time | std_fit_time | mean_score_time | std_score_time | param_mlpclassifier__solver | param_mlpclassifier__max_iter | param_mlpclassifier__learning_rate_init | param_mlpclassifier__learning_rate | param_mlpclassifier__hidden_layer_sizes | param_mlpclassifier__alpha | param_mlpclassifier__activation | params | split0_test_score | split1_test_score | split2_test_score | split3_test_score | split4_test_score | mean_test_score | std_test_score | rank_test_score | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 7 | 1.267821 | 0.067580 | 0.006274 | 0.002476 | adam | 1000 | 0.0010 | constant | (50,) | 0.00001 | logistic | {'mlpclassifier__solver': 'adam', 'mlpclassifi... | 0.909091 | 1.000000 | 0.954545 | 0.837209 | 0.883721 | 0.916913 | 0.056277 | 1 |
| 29 | 0.184175 | 0.014994 | 0.004768 | 0.000138 | adam | 1000 | 0.0100 | constant | (100,) | 0.00100 | relu | {'mlpclassifier__solver': 'adam', 'mlpclassifi... | 0.931818 | 0.977273 | 0.931818 | 0.837209 | 0.883721 | 0.912368 | 0.047830 | 2 |
| 6 | 2.102047 | 0.056905 | 0.005138 | 0.000101 | adam | 1000 | 0.0010 | invscaling | (200,) | 0.00001 | logistic | {'mlpclassifier__solver': 'adam', 'mlpclassifi... | 0.909091 | 0.954545 | 0.954545 | 0.837209 | 0.883721 | 0.907822 | 0.044575 | 3 |
| 3 | 1.688232 | 0.058199 | 0.005250 | 0.000317 | adam | 1000 | 0.0010 | invscaling | (100,) | 0.00001 | logistic | {'mlpclassifier__solver': 'adam', 'mlpclassifi... | 0.909091 | 0.954545 | 0.954545 | 0.837209 | 0.883721 | 0.907822 | 0.044575 | 3 |
| 21 | 8.279391 | 0.592481 | 0.007698 | 0.003196 | adam | 1000 | 0.0001 | invscaling | (300,) | 0.00001 | tanh | {'mlpclassifier__solver': 'adam', 'mlpclassifi... | 0.909091 | 0.954545 | 0.954545 | 0.837209 | 0.883721 | 0.907822 | 0.044575 | 3 |
# Convertir columnas con objetos no ploteables a string para graficar
results_df["param_mlpclassifier__hidden_layer_sizes"] = results_df["param_mlpclassifier__hidden_layer_sizes"].astype(str)
results_df["param_mlpclassifier__learning_rate_init"] = results_df["param_mlpclassifier__learning_rate_init"].astype(str)
results_df["param_mlpclassifier__activation"] = results_df["param_mlpclassifier__activation"].astype(str)
results_df["param_mlpclassifier__alpha"] = results_df["param_mlpclassifier__alpha"].astype(str)
# Graficar usando seaborn.relplot con columnas por tipo de activación
sns.set(style="whitegrid")
g = sns.relplot(
data=results_df,
x="param_mlpclassifier__hidden_layer_sizes", y="mean_test_score",
hue="param_mlpclassifier__learning_rate_init", style="param_mlpclassifier__activation", col="param_mlpclassifier__alpha",
kind="line", palette="tab10",
height=5, aspect=0.75
)
plt.tight_layout()
random_search.best_params_
{'mlpclassifier__solver': 'adam',
'mlpclassifier__max_iter': 1000,
'mlpclassifier__learning_rate_init': 0.001,
'mlpclassifier__learning_rate': 'constant',
'mlpclassifier__hidden_layer_sizes': (50,),
'mlpclassifier__alpha': 1e-05,
'mlpclassifier__activation': 'logistic'}
Vamos a tratar el problema de detección de humedad como un problema de regresión.
En este caso el modelo va a devolver un valor predicho $\hat y$ continuo que podemos acotar y redondear al entero más cercano.
En una regresión normal, el modelo predice valores continuos en un rango indefinido, como $(-\infty, \infty)$. Pero en muchos casos, sabemos de antemano que la variable a predecir está dentro de ciertos límites.
En nuestro caso, queremos predecir la humedad, y sabemos que solo toma valores entre 10 y 16 (quizá por discretización previa o límites físicos del sensor).
La forma más elegante en una red neuronal es usar una función de activación en la salida que esté acotada, y luego escalar esa salida al rango deseado.
Si la salida del modelo pasa por una sigmoid, entonces está en $(0, 1)$. Para transformarla al rango $[a, b]$, usamos:
Para transformar la salida a $[10, 16]$, simplemente usamos:
Lambda(lambda x: 10 + 6 * sigmoid(x))
Donde:
10 es el límite inferior6 es la amplitud del rango: $16 - 10 = 6$sigmoid(x) asegura que el resultado final esté en $[10, 16]$Ahora sí, el código completo con comentarios:
from tensorflow.keras.models import Sequential
from tensorflow.keras.layers import Dense, Lambda
from tensorflow.keras.optimizers import Adam
import tensorflow.keras.backend as K
# Definir modelo de regresión acotada
def build_model():
model = Sequential([
# Capa oculta 1: 512 neuronas con ReLU
Dense(512, activation='relu', input_shape=(X_train_scaled.shape[1],)),
# Capa oculta 2: 256 neuronas con ReLU
Dense(256, activation='relu'),
# Capa de salida: un solo valor (regresión)
Dense(1),
# Lambda: transforma la salida al rango [10, 16] usando sigmoide
Lambda(lambda x: 10 + 6 * K.sigmoid(x))
])
# Compilación del modelo
model.compile(
optimizer=Adam(learning_rate=0.001),
loss='mse', # Error cuadrático medio, típico en regresión
metrics=['mae'] # Error absoluto medio, más interpretable
)
return model
model = build_model()
history = model.fit(
X_train_scaled, y_train,
validation_split=0.1, # 10% para validación
epochs=50,
batch_size=32,
verbose=1 # Cambia a 0 si no quieres ver la barra de progreso
)
Para evaluar el modelo como clasificación (ya que la humedad son enteros 10–16):
import numpy as np
from sklearn.metrics import classification_report, ConfusionMatrixDisplay
# Predicción
y_pred = model.predict(X_test_scaled)
y_pred_rounded = np.round(y_pred).astype(int)
y_pred_rounded = np.clip(y_pred_rounded, 10, 16)
# Evaluación como clasificación
print(classification_report(y_test, y_pred_rounded))
ConfusionMatrixDisplay.from_predictions(y_test, y_pred_rounded, labels=range(10, 17)).plot()
Este enfoque permite:
✅ Modelar una regresión con salidas estrictamente dentro de un rango
✅ Usar una red neuronal para capturar relaciones no lineales
✅ Interpretar y evaluar el modelo también como un clasificador discreto si lo deseas
✅ Evitar el uso de clip() o if innecesarios
import pandas as pd
import numpy as np
from sklearn.model_selection import train_test_split
from sklearn.preprocessing import StandardScaler
import tensorflow as tf
from tensorflow.keras.models import Sequential
from tensorflow.keras.layers import Dense, Lambda
from tensorflow.keras.optimizers import Adam
import tensorflow.keras.backend as K
# Load data
data = pd.read_csv('https://raw.githubusercontent.com/marsgr6/r-scripts/master/data/G03_cropG_H_660_660_44_bins.csv')
data['humidity'] = data['humidity'].astype(int)
X = data.drop(columns='humidity')
y = data['humidity']
# Split and scale
X_train, X_test, y_train, y_test = train_test_split(X, y, test_size=0.2, random_state=42)
scaler = StandardScaler()
X_train_scaled = scaler.fit_transform(X_train)
X_test_scaled = scaler.transform(X_test)
def build_model():
model = Sequential([
# First hidden layer with 256 neurons and ReLU
Dense(512, activation='relu', input_shape=(X_train_scaled.shape[1],)),
# Second hidden layer
Dense(256, activation='relu'),
# Output layer
Dense(1),
# Lambda layer using sigmoid to ensure output ∈ (10, 16)
Lambda(lambda x: 10 + 6 * K.sigmoid(x)) # Output bounded in [10, 16]
])
# Compile model
model.compile(optimizer=Adam(learning_rate=0.001), loss='mse', metrics=['mae'])
return model
# Build and train
model = build_model()
history = model.fit(X_train_scaled, y_train, validation_split=0.1, epochs=50, batch_size=32, verbose=0)
# Predict and round to valid integers
y_pred = model.predict(X_test_scaled)
y_pred_rounded = np.round(y_pred).astype(int)
y_pred_rounded = np.clip(y_pred_rounded, 10, 16)
# Evaluate
from sklearn.metrics import mean_squared_error, r2_score
print("RMSE:", mean_squared_error(y_test, y_pred_rounded))
print("R2 score:", r2_score(y_test, y_pred_rounded))
# Extract loss values
train_loss = history.history['loss']
val_loss = history.history['val_loss']
train_mae = history.history['mae']
val_mae = history.history['val_mae']
# Plot loss
plt.figure(figsize=(12, 5))
plt.subplot(1, 2, 1)
plt.plot(train_loss, label='Train Loss')
plt.plot(val_loss, label='Validation Loss')
plt.title('Loss over Epochs')
plt.xlabel('Epoch')
plt.ylabel('MSE Loss')
plt.legend()
# Plot MAE
plt.subplot(1, 2, 2)
plt.plot(train_mae, label='Train MAE')
plt.plot(val_mae, label='Validation MAE')
plt.title('MAE over Epochs')
plt.xlabel('Epoch')
plt.ylabel('Mean Absolute Error')
plt.legend()
plt.tight_layout()
2/2 ━━━━━━━━━━━━━━━━━━━━ 0s 87ms/step RMSE: 0.3409090909090909 R2 score: 0.9067796610169492
reg_results = pd.DataFrame({'Observed humidity': y_test,
'Predicted humidity': y_pred.flatten(),
'Rounded humidity': y_pred_rounded.flatten()})
reg_results.describe()
| Observed humidity | Predicted humidity | Rounded humidity | |
|---|---|---|---|
| count | 44.000000 | 44.000000 | 44.000000 |
| mean | 13.454545 | 13.516138 | 13.477273 |
| std | 1.934444 | 1.810006 | 1.836182 |
| min | 10.000000 | 10.073403 | 10.000000 |
| 25% | 12.000000 | 12.081210 | 12.000000 |
| 50% | 14.000000 | 14.015269 | 14.000000 |
| 75% | 15.000000 | 15.073646 | 15.000000 |
| max | 16.000000 | 15.997149 | 16.000000 |
sns.scatterplot(data=reg_results, x="Observed humidity",
y='Predicted humidity',
hue=pd.Categorical(reg_results['Observed humidity']))
<Axes: xlabel='Observed humidity', ylabel='Predicted humidity'>
from sklearn.metrics import confusion_matrix, ConfusionMatrixDisplay, classification_report
import numpy as np
import matplotlib.pyplot as plt
# Round and clip predictions (if not already done)
y_pred_rounded = np.round(y_pred).astype(int)
y_pred_rounded = np.clip(y_pred_rounded, 10, 16)
# Labels: valid humidity levels
labels = list(range(10, 17))
# Compute confusion matrix
cm = confusion_matrix(y_test, y_pred_rounded, labels=labels)
# Display nicely with sklearn
disp = ConfusionMatrixDisplay(confusion_matrix=cm, display_labels=labels)
disp.plot(cmap='Blues', xticks_rotation=0)
plt.title('Confusion Matrix - Rounded Humidity Classification')
plt.grid(False)
# Optional: print classification report
print("Classification Report:\n")
print(classification_report(y_test, y_pred_rounded, labels=labels))
Classification Report:
precision recall f1-score support
10 1.00 0.80 0.89 5
11 1.00 1.00 1.00 3
12 0.71 1.00 0.83 5
13 1.00 0.75 0.86 8
14 0.86 0.75 0.80 8
15 0.58 1.00 0.74 7
16 0.80 0.50 0.62 8
accuracy 0.80 44
macro avg 0.85 0.83 0.82 44
weighted avg 0.84 0.80 0.79 44
La validación cruzada (Cross Validation) es una técnica que permite evaluar un modelo de forma más robusta al usar diferentes particiones del conjunto de datos. En el caso de 5 folds, seguimos este proceso:
Durante cada iteración:
✅ Reduce la posibilidad de que el modelo solo funcione bien por casualidad en una división específica. ✅ Aumenta la validez estadística de tus métricas (ej. accuracy, RMSE, R²). ✅ Útil especialmente cuando no tienes demasiados datos.
En este caso, el modelo:
sigmoid escalada.Para cada uno de los 5 folds:
Se calcula el accuracy como si fuera un problema de clasificación:
$$ \text{accuracy} = \frac{\text{predicciones correctas}}{\text{total de predicciones}} $$
Una lista como esta:
Fold 1: Accuracy = 0.78
Fold 2: Accuracy = 0.75
Fold 3: Accuracy = 0.77
Fold 4: Accuracy = 0.76
Fold 5: Accuracy = 0.80
Promedio: 0.772 ± 0.018
Este promedio nos da una medida más generalizable del rendimiento del modelo que una sola corrida con train_test_split.
La validación cruzada te permite:
Y como nuestro modelo está acotado (bounded regression), usar validación cruzada + rounding te permite obtener métricas de clasificación aunque el modelo sea regresivo.
Dropout?¶Dropout es una técnica de regularización para redes neuronales profundas. Durante el entrenamiento, desactiva aleatoriamente un porcentaje de neuronas en cada capa en cada paso de entrenamiento.
Dropout?¶| Problema | ¿Cómo ayuda Dropout? |
|---|---|
| Sobreajuste (overfitting) | Evita que la red aprenda "de memoria" el conjunto de entrenamiento |
| Alta complejidad del modelo | Fuerza al modelo a ser más robusto al impedir que dependa de rutas específicas |
| Poca generalización | Promueve la combinación de múltiples subredes, mejorando la capacidad de generalizar |
| Redes muy profundas | Las redes grandes tienden a sobreajustar; Dropout es simple y efectivo |
Durante el entrenamiento:
p (por ejemplo, p = 0.3)early stopping, L2, etc.)from tensorflow.keras.layers import Dropout
model = Sequential([
Dense(128, activation='relu', input_shape=(X.shape[1],)),
Dropout(0.3), # Desactiva el 30% de las neuronas durante entrenamiento
Dense(64, activation='relu'),
Dropout(0.3),
Dense(1)
])
import pandas as pd
import numpy as np
from sklearn.model_selection import KFold
from sklearn.preprocessing import StandardScaler
from sklearn.metrics import accuracy_score
import tensorflow as tf
from tensorflow.keras.models import Sequential
from tensorflow.keras.layers import Dense, Lambda
from tensorflow.keras.optimizers import Adam
import tensorflow.keras.backend as K
from tensorflow.keras.layers import Dropout
# Load data
data = pd.read_csv('https://raw.githubusercontent.com/marsgr6/r-scripts/master/data/G03_cropG_H_660_660_44_bins.csv')
data['humidity'] = data['humidity'].astype(int)
X = data.drop(columns='humidity').to_numpy()
y = data['humidity'].to_numpy()
# K-Fold setup
kf = KFold(n_splits=5, shuffle=True, random_state=42)
accuracy_scores = []
fold = 1
for train_index, test_index in kf.split(X):
print(f"\n🔁 Fold {fold}")
# Split
X_train, X_test = X[train_index], X[test_index]
y_train, y_test = y[train_index], y[test_index]
# Scale
scaler = StandardScaler()
X_train_scaled = scaler.fit_transform(X_train)
X_test_scaled = scaler.transform(X_test)
# Define model
def build_model():
model = Sequential([
Dense(512, activation='relu', input_shape=(X_train_scaled.shape[1],)),
Dropout(0.3), # Apaga el 30% de las neuronas aleatoriamente
Dense(256, activation='relu'),
Dropout(0.3),
Dense(1),
Lambda(lambda x: 10 + 6 * K.sigmoid(x)) # Output in [10, 16]
])
model.compile(optimizer=Adam(learning_rate=0.001), loss='mse', metrics=['mae'])
return model
# Train
model = build_model()
model.fit(X_train_scaled, y_train, validation_split=0.1, epochs=50, batch_size=32, verbose=0)
# Predict and round
y_pred = model.predict(X_test_scaled)
y_pred_rounded = np.round(y_pred).astype(int)
y_pred_rounded = np.clip(y_pred_rounded, 10, 16)
# Accuracy as classification
acc = accuracy_score(y_test, y_pred_rounded)
accuracy_scores.append(acc)
print(f"✅ Accuracy: {acc:.3f}")
fold += 1
# Summary
print("\n📊 Accuracy from 5-fold cross-validation:")
for i, acc in enumerate(accuracy_scores, 1):
print(f"Fold {i}: {acc:.3f}")
print(f"\n🔎 Mean Accuracy: {np.mean(accuracy_scores):.3f} ± {np.std(accuracy_scores):.3f}")
🔁 Fold 1 2/2 ━━━━━━━━━━━━━━━━━━━━ 0s 58ms/step ✅ Accuracy: 0.818 🔁 Fold 2
WARNING:tensorflow:5 out of the last 5 calls to <function TensorFlowTrainer.make_predict_function.<locals>.one_step_on_data_distributed at 0x7da83fb0cc20> triggered tf.function retracing. Tracing is expensive and the excessive number of tracings could be due to (1) creating @tf.function repeatedly in a loop, (2) passing tensors with different shapes, (3) passing Python objects instead of tensors. For (1), please define your @tf.function outside of the loop. For (2), @tf.function has reduce_retracing=True option that can avoid unnecessary retracing. For (3), please refer to https://www.tensorflow.org/guide/function#controlling_retracing and https://www.tensorflow.org/api_docs/python/tf/function for more details.
1/2 ━━━━━━━━━━━━━━━━━━━━ 0s 65ms/step
WARNING:tensorflow:6 out of the last 6 calls to <function TensorFlowTrainer.make_predict_function.<locals>.one_step_on_data_distributed at 0x7da83fb0cc20> triggered tf.function retracing. Tracing is expensive and the excessive number of tracings could be due to (1) creating @tf.function repeatedly in a loop, (2) passing tensors with different shapes, (3) passing Python objects instead of tensors. For (1), please define your @tf.function outside of the loop. For (2), @tf.function has reduce_retracing=True option that can avoid unnecessary retracing. For (3), please refer to https://www.tensorflow.org/guide/function#controlling_retracing and https://www.tensorflow.org/api_docs/python/tf/function for more details.
2/2 ━━━━━━━━━━━━━━━━━━━━ 0s 65ms/step ✅ Accuracy: 0.977 🔁 Fold 3 2/2 ━━━━━━━━━━━━━━━━━━━━ 0s 61ms/step ✅ Accuracy: 0.727 🔁 Fold 4 2/2 ━━━━━━━━━━━━━━━━━━━━ 0s 61ms/step ✅ Accuracy: 0.860 🔁 Fold 5 2/2 ━━━━━━━━━━━━━━━━━━━━ 0s 108ms/step ✅ Accuracy: 0.744 📊 Accuracy from 5-fold cross-validation: Fold 1: 0.818 Fold 2: 0.977 Fold 3: 0.727 Fold 4: 0.860 Fold 5: 0.744 🔎 Mean Accuracy: 0.825 ± 0.090
import pandas as pd
import numpy as np
from sklearn.model_selection import StratifiedKFold, cross_val_score
from sklearn.neural_network import MLPClassifier
from sklearn.pipeline import make_pipeline
from sklearn.preprocessing import StandardScaler
import seaborn as sns
import matplotlib.pyplot as plt
# -------------------------------
# 1. Cargar y preparar los datos
# -------------------------------
data = pd.read_csv('https://raw.githubusercontent.com/marsgr6/r-scripts/master/data/G03_cropG_H_660_660_44_bins.csv')
# Asegurarse de que la etiqueta sea categórica (str o int para clasificación)
data['humidity'] = data['humidity'].astype(str)
# Separar características y etiquetas
X = data.drop(columns='humidity')
y = data['humidity']
# -------------------------------
# 2. Definir el mejor modelo MLP
# -------------------------------
best_MLP_pipeline = make_pipeline(
StandardScaler(),
MLPClassifier(
activation='relu',
alpha=0.0001,
hidden_layer_sizes=(100,),
learning_rate_init=0.001,
max_iter=1000,
random_state=42
)
)
# -------------------------------
# 3. Validación cruzada (5 folds)
# -------------------------------
cv_method = StratifiedKFold(n_splits=5, shuffle=True, random_state=42)
# Evaluar accuracy por fold
scores_class = cross_val_score(best_MLP_pipeline, X, y, cv=cv_method, scoring='accuracy')
# -------------------------------
# 4. Resultados
# -------------------------------
print("🎯 Accuracy por fold:", scores_class)
print(f"📊 Accuracy promedio: {scores_class.mean():.3f} ± {scores_class.std():.3f}")
# -------------------------------
# 5. Visualización
# -------------------------------
# Crear DataFrame largo para comparar
df_compare = pd.DataFrame({
'Accuracy': np.concatenate([scores_class, accuracy_scores]),
'Modelo': ['MLPClassifier (SKLearn)'] * len(scores_class) + ['Regresión Acotada (Keras)'] * len(accuracy_scores)
})
# Boxplot comparativo
plt.figure(figsize=(8, 6))
sns.boxplot(x='Modelo', y='Accuracy', data=df_compare)
sns.stripplot(x='Modelo', y='Accuracy', data=df_compare, color='black', size=6, jitter=True, alpha=0.7)
sns.lineplot(x='Modelo', y='Accuracy', data=df_compare, linestyle='--', color='red', err_style='bars')
plt.title("Comparación de Accuracy (5-Fold Cross-Validation)")
plt.ylim(0.6, 1.0)
plt.grid(True)
plt.show()
🎯 Accuracy por fold: [0.93181818 0.95454545 0.97727273 0.88372093 0.90697674] 📊 Accuracy promedio: 0.931 ± 0.033
df_compare.groupby('Modelo').describe()
| Accuracy | ||||||||
|---|---|---|---|---|---|---|---|---|
| count | mean | std | min | 25% | 50% | 75% | max | |
| Modelo | ||||||||
| MLPClassifier (SKLearn) | 5.0 | 0.930867 | 0.037110 | 0.883721 | 0.906977 | 0.931818 | 0.954545 | 0.977273 |
| Regresión Acotada (Keras) | 5.0 | 0.825476 | 0.100712 | 0.727273 | 0.744186 | 0.818182 | 0.860465 | 0.977273 |
| Característica | MLPClassifier (Scikit-learn) | Regresión Acotada (Keras) |
|---|---|---|
| Tipo de modelo | Clasificación directa | Regresión continua acotada |
| Salida del modelo | Clases discretas (10 a 16) | Valores continuos en [10, 16] |
| Métrica optimizada durante el entrenamiento | accuracy implícitamente |
mse (error cuadrático medio) |
| Precisión promedio (5 folds) | ~0.93 | ~0.83 |
| Estabilidad entre folds | Alta (baja dispersión) | Baja (mayor variabilidad) |
| Ventaja principal | Mejor para predecir clases exactas | Útil si interesa el valor numérico real |
| Desventaja principal | No da predicción numérica continua | No optimiza directamente la clasificación |
| Adecuado para... | Problemas de clasificación clara | Problemas de predicción continua con límites conocidos |
MLPClassifier es superior por precisión y estabilidad.ML tutorials from www.featureranking.com